Preliminary investigation of fish diversity in middle and lower reaches of Pearl River based on environmental DNA technology
-
摘要:
通过环境DNA技术 (Environmental DNA, eDNA) 检测珠江中下游鱼类生物多样性,探索珠江中下鱼类多样性监测和保护的新途径。2023年2月在珠江中下游设置了桂平、藤县、封开、德庆、肇庆和九江共6个采样点,通过水样采集及过滤、eDNA提取、遗传标记扩增及测序和数据库比对分析等流程检测鱼类多样性。结果表明,6个采样点共检测出30种鱼类,隶属于4目10科27属,其中土著鱼类26种,外来种4种。较已有传统调查数据新检出2种鱼类:美丽沙鳅 (Botia pulchra) 和齐氏罗非鱼 (Oceochromis zillii)。鱼类优势种为子陵吻鰕虎鱼 (Rhinogobius giurinus)、瓦氏黄颡鱼 (Pelteobagrus vachellii)、鲢 (Hypophthalmichthys molitrix)、尼罗罗非鱼 (O. nilotica)、齐氏罗非鱼、南方波鱼 (Rasbora steineri) 和鲤 (Cyprinus carpio)。根据Shannon指数和Simpson指数显示,eDNA检测九江和桂平站点的鱼类多样性最高,藤县的最低。作为一种新的检测方法,eDNA技术可用于快速检测珠江中下游鱼类的多样性及分布,在实际应用中可将eDNA技术与传统的监测方法相结合,以提供更全面的鱼类生物多样性数据信息。
-
关键词:
- 环境DNA (eDNA) /
- 鱼类多样性 /
- 珠江中下游
Abstract:To explore new ways for observing and protecting fish species diversity in the middle and lower reaches of the Pearl River, we used eDNA technology to detect fish species diversity in that river section. Six sampling localities, namely Guiping, Tengxian, Fengkai, Deqing, Zhaoqing and Jiujiang, were set up in February 2023. The fish diversity was detected by eDNA metabarcoding analysis that includes water collection, water filtration, eDNA extraction, genetic marker amplification, sequencing and bioinformatic analyses. The results show that 30 fish species had been detected in 6 sampling sites, belonging to 4 orders, 10 families and 27 genera, in which 26 were native species and 4 were non-native species. Compared with traditional survey reports, two new species (Botia pulchra and Oceochromis zillii) were detected. Rhinogobius giurinus, Pelteobagrus vachellii, Hypophthalmichthys molitrix, O. nilotica, O. zillii, Rasbora steineri and Cyprinus carpio were found at each sampling site, indicating that these species are the dominant species in the survey area. According to Shannon index and Simpson index, the fish diversity was highest in Jiujiang and Guiping, while lowest in Tengxian. As a new detection method, eDNA technology can efficiently investigate the fish biodiversity and distribution in the middle and lower reaches of the Pearl River. To sum up, eDNA technology can be combined with traditional fish resources monitoring methods to provide more comprehensive data information on fish species diversity.
-
鱼类是水生态系统的重要组成部分,不仅为人类提供了丰富的食物蛋白,也维护着水生态系统的稳定[1-2]。然而,受栖息地退化、过度捕捞、水污染、气候变化和外来物种入侵等因素的影响[1,3],鱼类生物多样性和渔业资源锐减,进而威胁水生态系统功能、渔业经济和人类生存[4-5]。对鱼类物种分布和种群动态的准确、及时地监测与评估显得尤为迫切,同时也可为渔业资源相关保护和管理决策的制定提供科学指导。利用传统鱼类监测方法,如电捕、网捕、陷阱诱捕等[6],虽可获得鱼类种类和种群的关键信息,但存在成本高、费时费力、调查范围有限[7]、破坏性大、稀有物种捕获率低[7-8]、形态鉴别困难[9]等问题。传统调查方法已无法满足及时、全面和准确的鱼类监测和评估要求。因此,迫切需要更准确、有效和经济的调查方法,以弥补渔业资源监测和管理方面的不足。
近年来,环境DNA (Environmental DNA, eDNA) 技术作为一种新兴的检测评估方法,被认为是生物多样性研究中发展和普及最快的方法之一[10-11]。eDNA是指存在于任何环境样品 (如水、冰、土壤、沉积物、生物膜和空气) 中的DNA的总和[7]。对于鱼类来说,eDNA通常是鱼类体细胞释放到水体中的胞内遗传物质和细胞结构裂解或死亡后释放到水体中的胞外DNA[12-13]。eDNA技术通过直接提取环境样品中的DNA,利用特异性引物进行PCR扩增和高通量测序,对环境样本中存在的多个目标物种进行识别[14]。基于eDNA技术的调查方法具有灵敏度高、分辨率高、效率高、成本低和无损伤等优点,是解决渔业资源调查和管理难题的有效方法[15-16]。eDNA技术首次在鱼类研究中的应用是关于特定物种的监测[17]和鱼类多样性研究[18]。目前,eDNA技术在渔业领域的应用发展迅速,已广泛应用于渔业管理、鱼类种类及多样性监测、资源量评估和种群分布等[8,19-21]。
珠江是中国南方第一大河,全长2 214 km,流域面积45.37万km2,年径流量约3 300亿m3[22]。珠江地处热带、亚热带季风气候区,气候温和多雨,地形地貌复杂多样[23]。独特的生境孕育了珠江丰富的鱼类资源,鱼类物种多样性在全球大河流域中排名第四,特有种类数位居第二[24]。据统计,珠江水系记录鱼类达682种,其中特有种242种 (亚种),种类数和特有种数均居中国各流域之首。近几十年来,由于人类活动影响加剧,导致珠江生态环境退化、鱼类适宜栖息地丧失和水生生物入侵等,造成鱼类种群衰减、物种丧失和鱼类群落结构与功能改变[25-27]。为此,政府和管理部门实施了多项渔业资源养护措施,包括建立禁渔期制度、开展增殖放流活动和划定水产种质资源保护区等,以期改善珠江流域鱼类生物多样性和渔业资源现状[1,28-29]。
珠江鱼类生物多样性和渔业资源保护亟需构建快速有效且环境友好的监测体系,为渔业保护和管理决策的制定及实施提供科学依据。本研究首次利用eDNA技术对珠江中下游鱼类多样性进行研究,旨在探讨该技术对检测珠江中下游鱼类生物多样性的适用性,为珠江鱼类生物多样性的监测及保护提供新的技术支持。
1. 材料与方法
1.1 样品采集
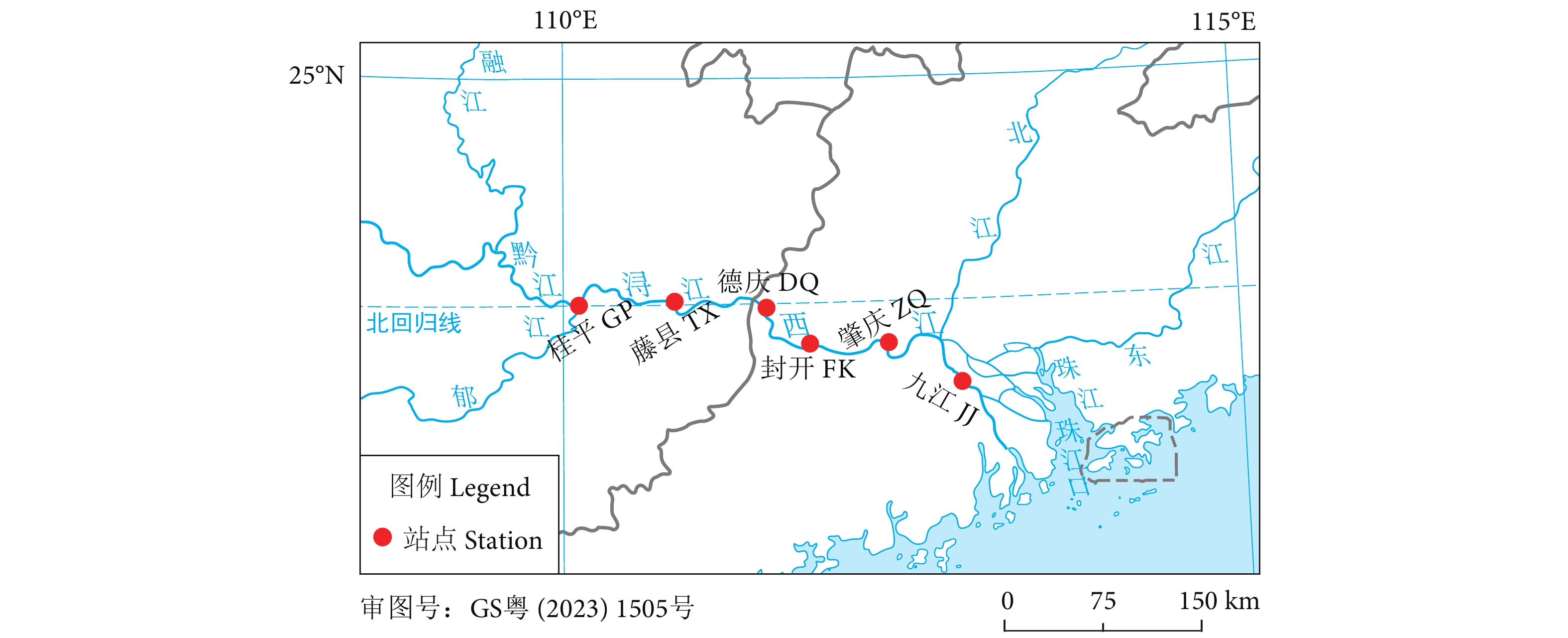
本次调查于2023年2月8—12日进行,在珠江中下游选取了桂平GP (110°07'34.45''E, 23°25'11.92''N)、藤县TX (110°50'5.06''E, 23°26'47.19''N)、封开FK (111°30'41.25''E, 23°23'35.73''N)、德庆DQ (111°49'53.35''E, 23°08'24.83''N)、肇庆ZQ (112°24'48.24''E, 23°07'58.23''N) 和九江JJ (112°56'40.33''E, 22°51'22.53''N) 6个采样点 (图1)。每个采样点采集3个重复样品,每个样品用采水器从表层水体采集2 L水样置于聚乙烯瓶中。采样人员佩戴一次性手套,采水器和采样瓶在使用前均经10% (w)的次氯酸钠消毒。所有样品均在24 h内使用0.45 μm混合纤维素滤膜 (Whatman,英国) 进行真空抽滤。为评估是否存在外源DNA污染,每次过滤设置1个阴性对照。每份样品过滤后,将滤膜置于4.5 mL无酶冻存管中于液氮中冷冻保存,并对过滤器材进行消毒和冲洗,避免样品间交叉污染。
1.2 eDNA提取
使用PowerWater DNA Isolation Kits (Qiagen公司) 按照试剂盒说明书提取滤膜中的DNA,用1% (w) 琼脂糖凝胶电泳检测提取DNA的质量。每份样品独立提取,并使用空白滤膜设置为阴性对照。将提取的DNA样品快速置于−20 ℃冷冻保存,直至PCR扩增。
1.3 遗传标记扩增及高通量测序
本研究使用鱼类eDNA宏条形码分析常用引物mlCOlintF (5'-GGWACWGGWTGAACWGTWTAYCCYCC-3') 和jgHCO219 (5'-TAIACYTCIGGRTGICCRAARAAYCA-3') 扩增线粒体COI基因,扩增序列长度约313 bp[30]。20 μL PCR扩增体系包括:2~5 μL模板DNA (10 ng·μL−1)、正反向引物各0.8 μL (5 μmol·L−1)、2 μL dNTPs、4 μL 5×FastPfu缓冲液、0.4 μL FastPfu聚合酶,最后用ddH2O将体系补至20 μL。PCR反应程序为:95 ℃预变性5 min;95 ℃变性30 s,55 ℃退火30 s,72 ℃延伸45 s,35个循环;72 ℃延伸10 min。每个样品每次PCR反应均使用ddH2O为模板作阴性对照。每个样品进行3次重复扩增,并将同一样品的扩增产物混合,使用2% (w) 琼脂糖凝胶电泳检测PCR产物。所有阴性对照均无目的条带,表明无外源鱼类DNA污染;6个采样点的样品均得到可检测的PCR产物。PCR产物胶回收后送至上海凌恩生物科技有限公司通过Illumina NovaSeq 6000测序平台进行高通量测序。
1.4 数据库构建
2013—2019年,在珠江中下游采集78种共384尾鱼类样本,利用鱼类通用引物扩增603 bp线粒体COI基因序列[31]。此外,从NCBI (https://www.ncbi.nlm.nih.gov/) 数据库下载12种鱼类的COI基因序列进行补充,分别是叉尾斗鱼 (Macropodus opercularis)、大鳞副泥鳅 (Paramisgurnus dabryanus)、福建纹胸鮡 (Glyptothorax fukiensis)、虹彩光唇鱼 (Acrossocheilus iridescens)、黑鳍鳈 (Sarcocheilichthys nigripinnis)、黄鳝 (Monopterus albus)、横纹南鳅 (Schistura fasciolata)、金黄舌鰕虎鱼 (Glossogobius aureus)、美丽沙鳅 (Botia pulchra)、攀鲈 (Anabas testudineus)、三线舌鳎 (Cynoglossus trigrammus) 和云斑尖塘鳢 (Oxyeleotris marmoratus)。本研究利用这90种鱼类的COI基因序列构建珠江中下游鱼类DNA条形码数据库。利用MEGA-X软件,基于Kimura2-parameter (K2P) 模型对种间遗传距离 (Interspecific distance) 和种内遗传距离 (Intraspecific distance) 进行计算,并分析条形码间隙 (Barcode gap),以证实条形码数据库的可用性。此外,为了更直观地理解物种聚类模式,在MEGA-X软件中,基于K2P模型,自展值 (Bootstrap) 设置为1 000,构建Neighbor-Joining (NJ) 系统发育树。
1.5 数据分析
测序序列经过质控过滤、拼接后获得各样品的优质序列。序列按照相似性≥97%进行OTU (Operational taxonomic unit) 聚类分析,然后将OTU代表序列与自建的数据库进行比对、分类注释,并得到相应的OTU丰度表[32]。本研究以OTU聚类与注释结果为基础,进行物种组成和Alpha多样性分析。将OTU序列与数据库比对确定鱼类物种信息,阈值条件为Identity值≥97%,E-value<10−5。鱼类分类学信息参考《珠江鱼类志》[33]《中国内陆鱼类物种与分布》[34]和中国生物物种名录 (2022版)。Alpha多样性分析选取Chao1指数 (Chao1 index)、香农指数 (Shannon index)、辛普森指数 (Simpson index) 及覆盖度 (Coverage) 指数进行群落丰富度、多样性及覆盖度分析[32]。利用R软件vegan包,基于Bray-Curtis 距离矩阵进行主坐标分析 (Principal coordinates analysis, PCoA)[35],探讨不同采样点样本间群落组成空间分布差异。
2. 结果
2.1 条形码数据库
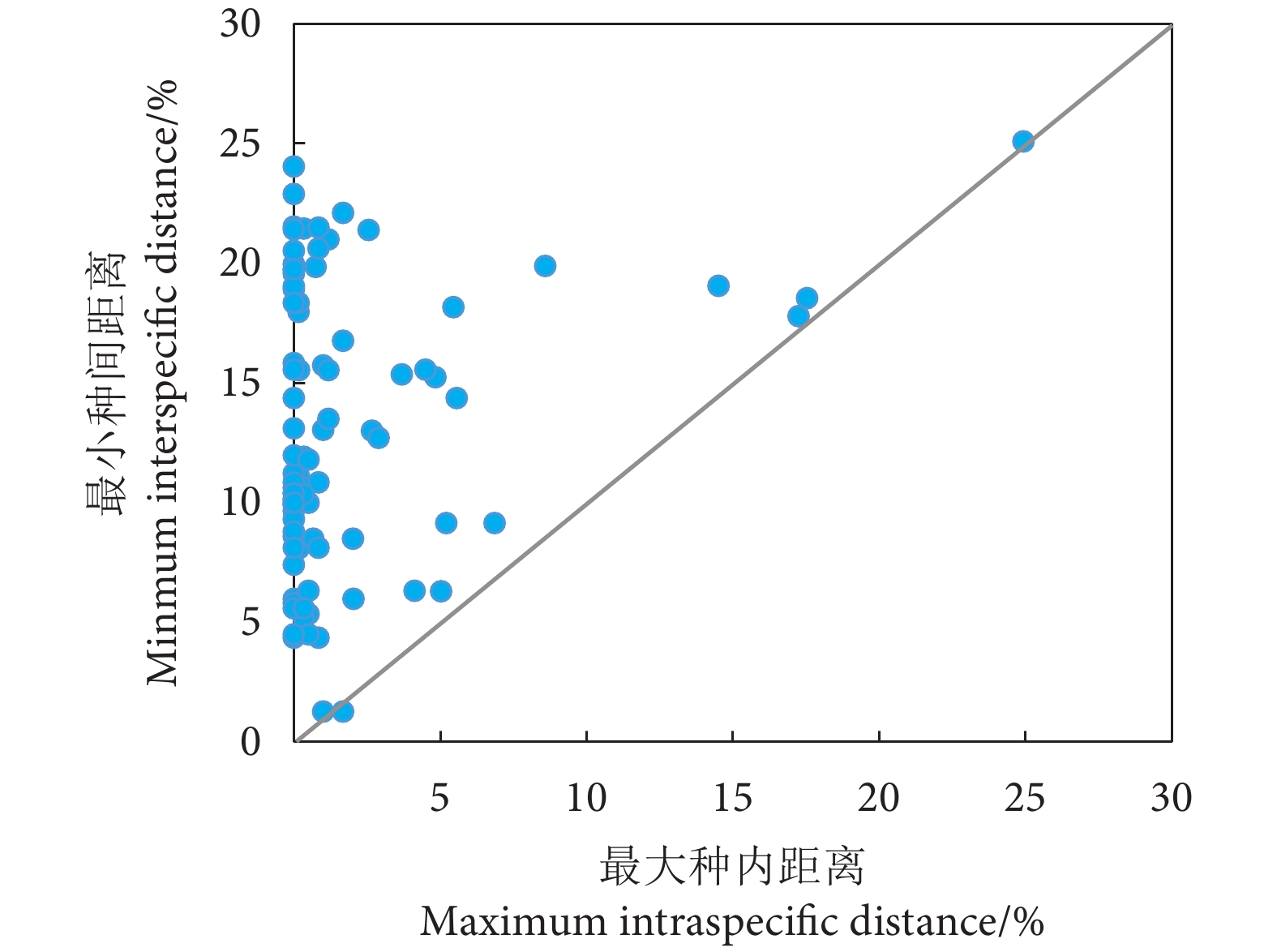
本研究构建的条形码数据库共463条COI序列,包括90种鱼类,隶属于17目32科75属。K2P遗传距离模型计算结果显示,基于数据库COI序列的种内遗传距离为0%~24.94%,平均值为0.95%;种间遗传距离为1.27%~34.93%,平均值为22.47%,种间平均遗传距离是种内的23.65倍。条形码间隙分析显示,除了黄尾鲴,数据库中其他物种的最小种间距离均大于最大种内距离,具有条形码间隙 (图2)。基于COI序列构建的NJ系统发育树见图3。
2.2 鱼类物种组成
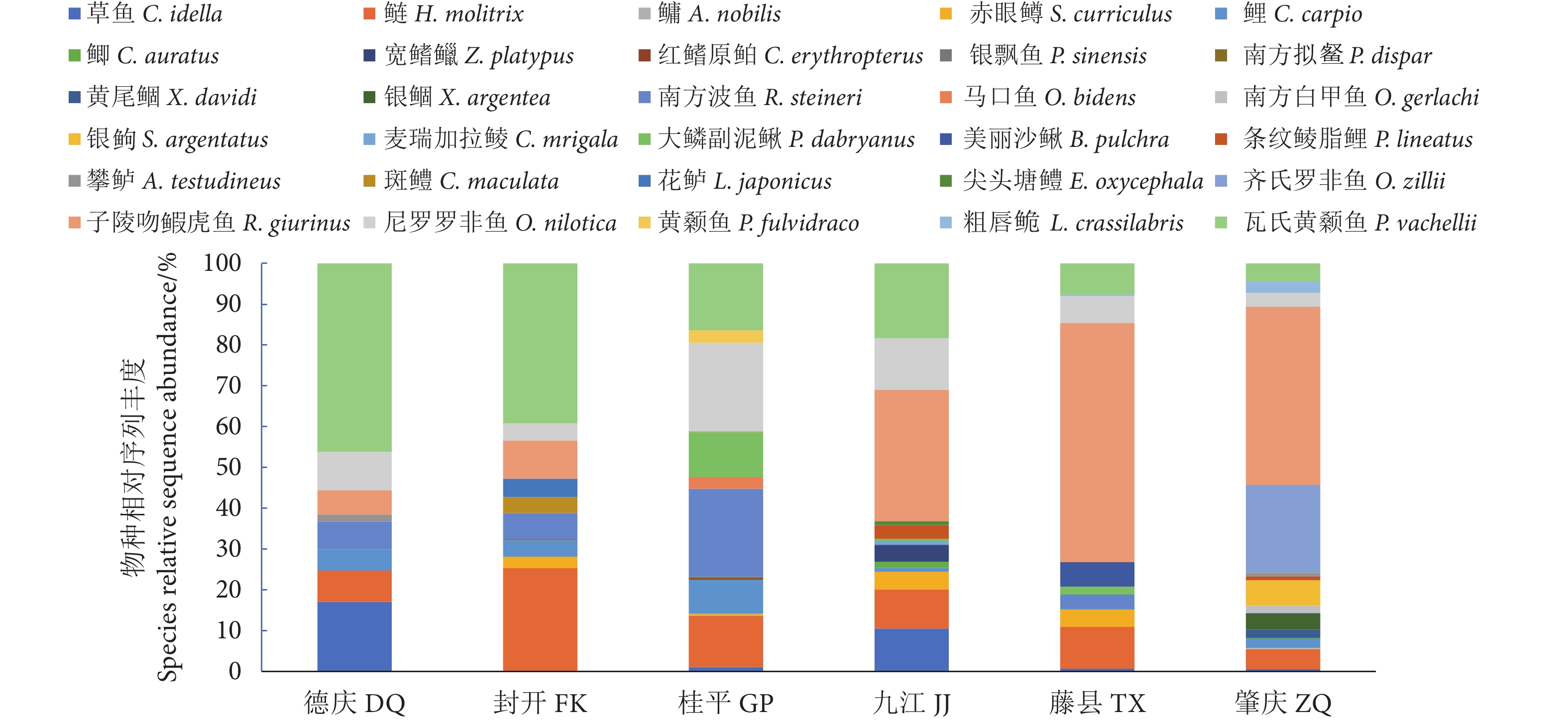
从6个采样点共获得13 025个OTU,其中九江的OTU数量最多 (6 476个),肇庆最少 (3 829个),其他采样点分别为德庆5 076个,封开5 012个,桂平4 244个,藤县3 889个;6个采样点共有的OTU为724个。对OTU进行注释,共获得已知鱼类物种序列2 613条,检出鱼类30种,隶属于4目10科27属,其中土著鱼类26种,外来种4种,各采样点的物种及序列数见表1。检出鱼类种类最多的为肇庆 (18种),其他分别为桂平13种、藤县11种、封开10种、德庆8种和九江14种。鱼类检测结果中鲤形目鲤科鱼类最多 (17种),占鱼类物种总数的56.67%;鲈形目和鲇形目分别为7和3种。基于各采样点的序列丰度,物种种类和相对序列丰度组成情况见图4。由图4可知,eDNA所检测序列数最多的7个物种依次为子陵吻鰕虎鱼 (Rhinogobius giurinus, 27.75%)、瓦氏黄颡鱼 (Pelteobagrus vachellii, 17.53%)、鲢 (Hypophthalmichthys molitrix, 11.71%)、尼罗罗非鱼 (Oceochromis nilotica, 8.50%)、齐氏罗非鱼 (O. zillii, 7.27%)、南方波鱼 (Rasbora steineri, 5.82%) 和鲤 (Cyprinus carpio, 3.41%);且除齐氏罗非鱼外,其他几种鱼类在各采样点均被检测到并显示出相对较高的序列丰度。
表 1 各采样点检测物种序列数Table 1. Number of reads detected for each species at each sampling station种类 Species 调查站位 Sampling station 德庆 DQ 封开 FK 桂平 GP 九江 JJ 藤县 TX 肇庆 ZQ 1 鲤形目 Cypriniformes 43 207 266 105 81 198 1.1鲤科 Cyprinidae 43 207 216 103 57 198 1.1.1草鱼 Ctenopharyngodon idella 20 0 5 34 2 5 1.1.2鲢 Hypophthalmichthys molitrix 9 135 57 31 31 43 1.1.3鳙 Aristichthys nobilis 0 0 0 0 0 2 1.1.4赤眼鳟 Squaliobarbus curriculus 0 15 2 14 13 1 1.1.5鲤 Cyprinus carpio 6 21 38 3 1 20 1.1.6鲫 Carassius auratus 0 0 0 5 0 2 1.1.7宽鳍鱲 Zacco platypus 0 0 0 13 0 0 1.1.8红鳍原鲌 Cultrichthys erythropterus 0 0 1 0 0 0 1.1.9银飘鱼 Pseudolaubuca sinensis 0 2 0 0 0 0 1.1.10南方拟䱗 Pseudohemiculter dispar 0 0 2 0 0 0 1.1.11黄尾鲴 Xenocypris davidi 0 0 0 0 0 18 1.1.12银鲴 Xenocypris argentea 0 0 0 0 0 35 1.1.13南方波鱼 Rasbora steineri 8 34 98 1 10 1 1.1.14马口鱼 Opsariichthys bidens 0 0 13 0 0 0 1.1.15南方白甲鱼 Onychostoma gerlachi 0 0 0 0 0 16 1.1.16银鮈 Squalidus argentatus 0 0 0 0 0 55 1.1.17麦瑞加拉鲮▲ Cirrhinus mrigala 0 0 0 2 0 0 1.2花鳅科 Cobitidae 0 0 50 2 24 0 1.2.1大鳞副泥鳅 Paramisgurnus dabryanus 0 0 50 2 6 0 1.2.2美丽沙鳅 Botia pulchra 0 0 0 0 18 0 2脂鲤目 Characiformes 0 0 0 11 0 8 2.1鲮脂鲤科 Prochilodontidae 0 0 0 11 0 8 2.1.1条纹鲮脂鲤▲ Prochilodus lineatus 0 0 0 11 0 8 3鲈形目 Perciformes 20 117 99 148 197 615 3.1攀鲈科 Anabantidae 2 0 0 0 0 9 3.1.1攀鲈 Anabas testudineus 2 0 0 0 0 9 3.2鳢科 Channidae 0 21 0 0 0 0 3.2.1斑鳢 Channa maculata 0 21 0 0 0 0 3.3狼鲈科 Moronidae 0 24 0 0 0 0 3.3.1花鲈 Lateolabrax japonicus 0 24 0 0 0 0 3.4塘鳢科 Eleotridae 0 0 0 3 0 0 3.4.1尖头塘鳢 Eleotris oxycephala 0 0 0 3 0 0 3.5鰕虎科 Gobiidae 7 50 1 104 177 386 3.5.1子陵吻鰕虎鱼 Rhinogobius giurinus 7 50 1 104 177 386 3.6丽鱼科 Cichlidae 11 22 98 41 20 220 3.6.1齐氏罗非鱼▲ Oceochromis zillii 0 0 0 0 0 190 3.6.2尼罗罗非鱼▲ Oceochromis nilotica 11 22 98 41 20 30 4鲇形目 Siluriformes 54 209 88 59 24 64 4.1鲿科 Bagridae 54 209 88 59 24 64 4.1.1黄颡鱼 Pelteobagrus fulvidraco 0 0 14 0 0 0 4.1.2粗唇鮠 Leiocassis crassilabris 0 0 0 0 1 25 4.1.3瓦氏黄颡鱼 Pelteobagrus vachellii 54 209 74 59 23 39 注:▲. 外来物种。 Note: ▲. Alien species. 2.3 历史调查数据比较
根据珠江中下游鱼类调查文献[23,25,27,36-37],统计得出近十多年传统调查共捕获鱼类132种 (未统计未鉴定种),隶属于13目30科 (附录A,详见http://dx.doi.org/10.12131/20230111的资源附件)。本研究较传统调查资料新检出美丽沙鳅和齐氏罗非鱼2种鱼类。
2.4 多样性分析
对珠江中下游鱼类群落进行Alpha多样性分析,各样本的Chao1、Shannon和Simpson多样性指数及覆盖度Coverage计算值见表2。各采样点中,Shannon指数最高的为九江 (2.90),其次为桂平 (2.89),最低的为藤县 (2.15);Simpson指数最高的为桂平 (0.84),其次为九江 (0.82),最低的为藤县 (0.63)。各个样本的Coverage值范围为0.993 4~1.000 0,表明检测结果基本覆盖到了全部鱼类物种。
表 2 各样本Alpha多样性指数Table 2. Alpha diversity index of each sample样本
SampleChao1指数
Chao1香农指数
Shannon辛普森指数
Simpson覆盖度
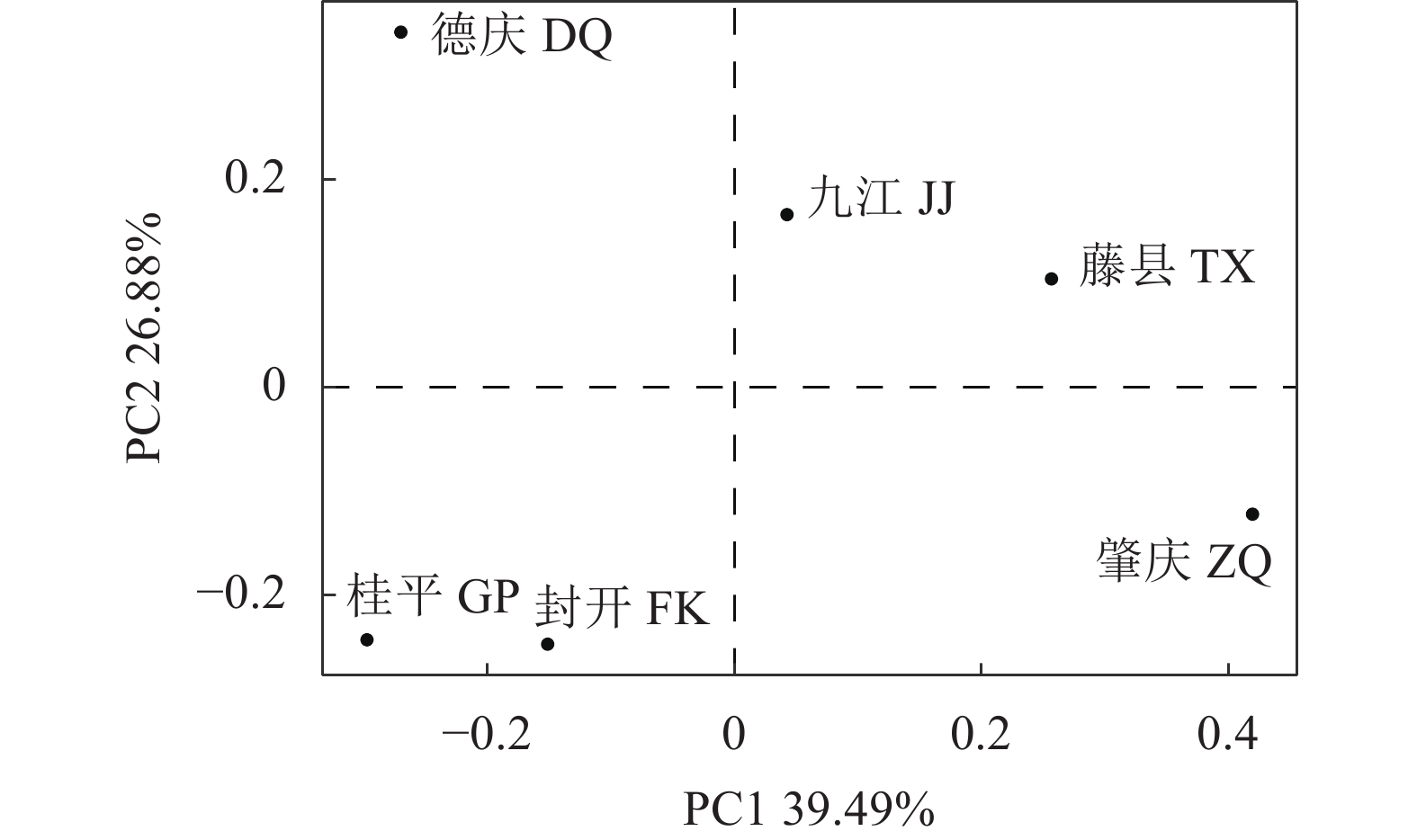
Coverage德庆 DQ 8.00 2.38 0.73 1.000 0 封开 FK 10.00 2.54 0.76 1.000 0 桂平 GP 13.33 2.89 0.84 0.995 6 九江 JJ 14.00 2.90 0.82 0.996 9 藤县 TX 11.50 2.15 0.63 0.993 4 肇庆 ZQ 18.33 2.73 0.75 0.997 7 基于eDNA检测的各采样点的序列丰度,采用Bray-Curtis距离矩阵进行PCoA分析 (图5),由图可知,桂平和封开站点距离较近,九江、藤县和肇庆站点距离较近,德庆站点与其他站点距离较远。表明桂平和封开站点具有相似的鱼类组成,九江、藤县和肇庆站点具有相似的鱼类组成,德庆站点具有与其他站点不同的鱼类组成。
3. 讨论
3.1 条形码数据库的适用性
目前COI条形码已广泛应用于鱼类种类鉴定中。Hebert等[38]提出了“10倍规则”的标准用于区分物种,即满足种间平均遗传距离大于种内平均遗传距离的10倍。蒋佩文等[39]在构建珠江河口鱼类COI条形码数据库时,其种间与种内平均遗传距离比值为127.7,符合“10倍规则”的标准,可实现珠江口鱼类物种的鉴定。郜星晨和姜伟[40]建立三峡鱼类COI条形码数据库,其种间平均遗传距离为种内的9.38倍,表明COI基因可以作为三峡库区常见鱼类鉴定的有效条形码基因。本研究中,COI序列种间平均遗传距离是种内的23.65倍,也符合“10倍规则”标准。此外,条形码间隙分析显示,除黄尾鲴外,其他种类均具有明显的条形码间隙。因此,COI序列在本研究中可满足鱼类物种的鉴别需求。
3.2 基于eDNA检测的鱼类组成
本研究首次使用eDNA技术分析了珠江中下游鱼类多样性,共检测出鱼类30种,其中鲤形目鲤科鱼类最多,占鱼类物种总数的56.67%,相较于传统调查方法[23,27],检出鱼类种类组成结构一致,均以鲤科鱼类为主,符合珠江水系鱼类区系组成特点[41]。传统调查方法研究显示,珠江中下游鱼类优势种包括广东鲂 (Megalobrama terminalis)、赤眼鳟 (Squaliobarbus curriculus)、鲮 (Cirrhinus molitorella)、鲤、子陵吻鰕虎鱼、鲢、草鱼 (Ctenopharyngodon idella)、瓦氏黄颡鱼和尼罗罗非鱼等[23,27,36]。本研究的鱼类优势种为子陵吻鰕虎鱼、瓦氏黄颡鱼、鲢、尼罗罗非鱼、齐氏罗非鱼、南方波鱼和鲤,优势种类与传统调查研究结果基本一致。但部分传统调查中的优势种类在本研究中未检测到,如广东鲂和鲮。这可能是由于本研究所用COI基因通用引物对广东鲂和鲮的扩增效率低,在低浓度DNA模板的条件下无法对目标基因序列进行扩增。其次,在设置调查站位时,综合考虑地理环境和有关鱼类生活习性,能够提高eDNA的物种检测效率[32]。本研究设置站位数量有限,未能充分考虑站位环境和鱼类生活习性。广东鲂为江河洄游性鱼类,4—8月为其产卵繁殖期,在西江的青皮塘和罗旁江段形成渔汛,珠江三角洲是其主要育肥和生长场所[42];珠江中下游鱼类优势种组成具有一定的季节差异,鲮主要是在秋季作为优势种[23],而本研究采样时间为春季。
已有研究表明,eDNA方法检测到的鱼类物种丰富度与基于传统的调查方法相似或更高[43-44]。例如,利用eDNA技术检测的鱼类种类数与使用刺网和电捕法在静态和激流水体中进行长期调查所检测的物种数相当[45]。但本研究检测到的鱼类物种数少于传统调查方法,李捷等[25] 2005—2008年调查鱼类97种,与本研究检出相同鱼类24种;李捷等[36] 2006—2008年调查鱼类81种,与本研究检出相同鱼类24种;李跃飞等[37] 2006—2007年调查鱼类75种,与本研究检出相同鱼类18种;帅方敏等[27] 2015年调查鱼类62种 (不包括未鉴定种),与本研究检出相同鱼类20种;张迎秋等[23] 2016—2018年调查鱼类96种 (不包括未鉴定种),与本研究检出相同鱼类26种。这可能由于本研究使用的COI通用引物没有足够的特异性,在原核生物和非鱼类真核生物DNA存在的情况下,引物对样品中的鱼类DNA扩增效率不高。已有研究表明,对于水体中低浓度的环境DNA模板,COI引物对鱼类DNA的扩增效率不高[46]。刘军等[47]研究发现,COI引物对鱼类样品和环境DNA样品均有较好的扩增效果,但测序结果显示COI引物从环境DNA中扩增的基因片段属于细菌微生物的基因片段,而未扩增出鱼类基因片段。此外,物种多样性调查结果与采样频次和eDNA数据库物种信息完整性有关。在生态环境的生物多样性调查中,特别是水生生态系统中,由于检测概率[48]、物种的稀有性[49]和采集强度[50]的影响,对物种多样性的评估可能受到限制,通过增加采样点和采样次数可以提高鱼类物种的检测效果[15]。基于eDNA技术的生物评价的有效性依赖于序列参考数据库的完整性,数据库缺少目标物种序列时会导致假阴性检测[51]。
相较于珠江河口水域eDNA研究,Zou等[52]在珠江河口水域的南沙湿地利用eDNA检测出35种淡水鱼类,与本研究相同的鱼类有7种:草鱼、鲢、赤眼鳟、鲤、南方白甲鱼 (Onychostoma gerlachi)、斑鳢 (Channa maculata)和尼罗罗非鱼。这可能与研究的区域、选用的引物和比对数据库的不同有关。Zou等[52]选用12S rRNA基因区的通用引物,利用GenBank数据库进行比对;本研究使用COI基因区的通用引物,比对自行构建的数据库。已有研究表明不同DNA区域 (如COI和12S rRNA基因) 元条形码引物在鱼类多样性和物种分辨率方面存在差异[53-54]。
3.3 鱼类多样性分析
本研究中Chao1指数范围为8.00~18.33,其中肇庆站点的值最高,表明该站点的群落丰富度最高。Shannon和Simpson指数可反映鱼类的多样性水平[55],本研究中Shannon和Simpson指数表明九江和桂平站点鱼类多样性最高。桂平站点位于郁江和黔江的交汇处,该江段为桂平东塔产卵场,是珠江流域最大的产卵场[56],水域环境复杂,是珠江众多珍稀特有鱼类的重要栖息地,因此具有较高的鱼类多样性。九江站点靠近珠江河口,受径流和潮汐相互作用,该水域咸淡水混合、物质交汇频繁、生产力丰富,是鱼类栖息、觅食和繁育的重要区域[57],因此鱼类生物多样性也较高。
鱼类群落结构的空间差异对于维持水生生态系统功能具有重要作用。在本研究中,基于环境DNA检测的鱼类物种序列丰度,通过PCoA分析显示桂平和封开站点具有相似的鱼类组成,藤县和九江站点具有相似的鱼类组成,但在地理位置上桂平和封开、藤县和九江站点相距较远。相反,地理位置较近的肇庆和德庆站点具有不同的鱼类组成。当然,仅基于本研究6个站点的数据不能充分展示珠江中下游鱼类群落空间分布格局,如需充分展示该区域的鱼类空间分布,需要设置更加密集的站位和更高频次的调查研究。
3.4 入侵物种和特有鱼类
防止有害物种入侵、保护稀有濒危物种是物种和生态系统监管的重要内容;eDNA技术由于其敏感性、快速性和特异性,因而在外来物种防控和珍稀濒危物种保护方面具有巨大的优势[20]。本研究中检测到4种外来入侵鱼类,分别为麦瑞加拉鲮 (Cirrhinus mrigala)、条纹鲮脂鲤 (Prochilodus lineatus)、齐氏罗非鱼和尼罗罗非鱼,且尼罗罗非鱼和齐氏罗非鱼已成为优势种类。罗非鱼主要是从养殖水体逃逸后,在珠江水系扩散并建群,目前已遍布整个流域并建立了自然群体[27,58-59]。珠江流域外来水生生物安全面临严重威胁,控制形势十分严峻。外来物种入侵是生物多样性丧失和全球同质化的主要原因之一[60],入侵物种会与土著种通过竞争成为优势种,从而对本地物种的种类和数量产生影响[61]。一旦外来物种入侵成功,不但控制成本高且根除的可能性很小[62]。eDNA技术增加了对入侵物种早期监测的可能性,降低了物种入侵的控制成本和生态影响。
eDNA技术检测灵敏度高,相较于传统调查方法显示出更高的检测效率和成本效益[63-64]。南方波鱼是珠江水系特有鱼类[36],属于山溪小型鱼类[65],喜栖息于溪流和水沟。由于调查所用网具和调查范围的限制,在近些年的传统调查研究中均未采集到该种鱼类;而在本研究的6个采样点中均可检出该种鱼类,说明珠江中下游存在一定种群数量的南方波鱼,也表明eDNA技术在特有鱼类的监测中具有一定优势。
4. 小结
eDNA技术具有成本低、检测灵敏度高、检测效率高和非破坏性采样等特点,为鱼类多样性监测和保护工作提供了新的选择。本研究首次利用eDNA技术检测了珠江中下游鱼类多样性,证明其对检测珠江中下游鱼类生物多样性及分布情况的可行性。理论上eDNA技术对鱼类多样性检测的高效性取决于一系列的生物和技术因素[13],无法完全替代传统鱼类调查方法。eDNA和传统鱼类调查方法各有其优势,可以提供重叠和互补信息,因此两者应该共同使用,以提供对鱼类生物多样性更全面的了解[66-67],也为制定旨在保护和增强水生态系统功能和恢复力的保护策略提供数据支撑。
-
表 1 各采样点检测物种序列数
Table 1 Number of reads detected for each species at each sampling station
种类 Species 调查站位 Sampling station 德庆 DQ 封开 FK 桂平 GP 九江 JJ 藤县 TX 肇庆 ZQ 1 鲤形目 Cypriniformes 43 207 266 105 81 198 1.1鲤科 Cyprinidae 43 207 216 103 57 198 1.1.1草鱼 Ctenopharyngodon idella 20 0 5 34 2 5 1.1.2鲢 Hypophthalmichthys molitrix 9 135 57 31 31 43 1.1.3鳙 Aristichthys nobilis 0 0 0 0 0 2 1.1.4赤眼鳟 Squaliobarbus curriculus 0 15 2 14 13 1 1.1.5鲤 Cyprinus carpio 6 21 38 3 1 20 1.1.6鲫 Carassius auratus 0 0 0 5 0 2 1.1.7宽鳍鱲 Zacco platypus 0 0 0 13 0 0 1.1.8红鳍原鲌 Cultrichthys erythropterus 0 0 1 0 0 0 1.1.9银飘鱼 Pseudolaubuca sinensis 0 2 0 0 0 0 1.1.10南方拟䱗 Pseudohemiculter dispar 0 0 2 0 0 0 1.1.11黄尾鲴 Xenocypris davidi 0 0 0 0 0 18 1.1.12银鲴 Xenocypris argentea 0 0 0 0 0 35 1.1.13南方波鱼 Rasbora steineri 8 34 98 1 10 1 1.1.14马口鱼 Opsariichthys bidens 0 0 13 0 0 0 1.1.15南方白甲鱼 Onychostoma gerlachi 0 0 0 0 0 16 1.1.16银鮈 Squalidus argentatus 0 0 0 0 0 55 1.1.17麦瑞加拉鲮▲ Cirrhinus mrigala 0 0 0 2 0 0 1.2花鳅科 Cobitidae 0 0 50 2 24 0 1.2.1大鳞副泥鳅 Paramisgurnus dabryanus 0 0 50 2 6 0 1.2.2美丽沙鳅 Botia pulchra 0 0 0 0 18 0 2脂鲤目 Characiformes 0 0 0 11 0 8 2.1鲮脂鲤科 Prochilodontidae 0 0 0 11 0 8 2.1.1条纹鲮脂鲤▲ Prochilodus lineatus 0 0 0 11 0 8 3鲈形目 Perciformes 20 117 99 148 197 615 3.1攀鲈科 Anabantidae 2 0 0 0 0 9 3.1.1攀鲈 Anabas testudineus 2 0 0 0 0 9 3.2鳢科 Channidae 0 21 0 0 0 0 3.2.1斑鳢 Channa maculata 0 21 0 0 0 0 3.3狼鲈科 Moronidae 0 24 0 0 0 0 3.3.1花鲈 Lateolabrax japonicus 0 24 0 0 0 0 3.4塘鳢科 Eleotridae 0 0 0 3 0 0 3.4.1尖头塘鳢 Eleotris oxycephala 0 0 0 3 0 0 3.5鰕虎科 Gobiidae 7 50 1 104 177 386 3.5.1子陵吻鰕虎鱼 Rhinogobius giurinus 7 50 1 104 177 386 3.6丽鱼科 Cichlidae 11 22 98 41 20 220 3.6.1齐氏罗非鱼▲ Oceochromis zillii 0 0 0 0 0 190 3.6.2尼罗罗非鱼▲ Oceochromis nilotica 11 22 98 41 20 30 4鲇形目 Siluriformes 54 209 88 59 24 64 4.1鲿科 Bagridae 54 209 88 59 24 64 4.1.1黄颡鱼 Pelteobagrus fulvidraco 0 0 14 0 0 0 4.1.2粗唇鮠 Leiocassis crassilabris 0 0 0 0 1 25 4.1.3瓦氏黄颡鱼 Pelteobagrus vachellii 54 209 74 59 23 39 注:▲. 外来物种。 Note: ▲. Alien species. 表 2 各样本Alpha多样性指数
Table 2 Alpha diversity index of each sample
样本
SampleChao1指数
Chao1香农指数
Shannon辛普森指数
Simpson覆盖度
Coverage德庆 DQ 8.00 2.38 0.73 1.000 0 封开 FK 10.00 2.54 0.76 1.000 0 桂平 GP 13.33 2.89 0.84 0.995 6 九江 JJ 14.00 2.90 0.82 0.996 9 藤县 TX 11.50 2.15 0.63 0.993 4 肇庆 ZQ 18.33 2.73 0.75 0.997 7 -
[1] CHEN Y S, QU X, XIONG F Y, et al. Challenges to saving China's freshwater biodiversity: fishery exploitation and landscape pressures[J]. Ambio, 2020, 49(4): 926-938. doi: 10.1007/s13280-019-01246-2
[2] HE Y F, WANG J W, LEK S, et al. Structure of endemic fish assemblages in the upper Yangtze River Basin[J]. River Res Appl, 2011, 27(1): 59-75. doi: 10.1002/rra.1339
[3] REID A J, CARLSON A K, CREED I F, et al. Emerging threats and persistent conservation challenges for freshwater biodiversity[J]. Biol Rev, 2019, 94(3): 849-873. doi: 10.1111/brv.12480
[4] COULTHARD S, JOHNSON D, MCGREGOR J A. Poverty, sustainability and human wellbeing: a social wellbeing approach to the global fisheries crisis[J]. Global Environ Chang, 2011, 21(2): 453-463. doi: 10.1016/j.gloenvcha.2011.01.003
[5] DUDGEON D. Multiple threats imperil freshwater biodiversity in the Anthropocene[J]. Curr Biol, 2019, 29(19): 960-967. doi: 10.1016/j.cub.2019.08.002
[6] BONAR S A, MERCADO-SILVA N, HUBERT W A, et al. Standard methods for sampling freshwater fishes: opportunities for international collaboration[J]. Fisheries, 2017, 42(3): 150-156. doi: 10.1080/03632415.2017.1276352
[7] YAO M, ZHANG S, LU Q, et al. Fishing for fish environmental DNA: ecological applications, methodological considerations, surveying designs, and ways forward[J]. Mol Ecol, 2022, 31(20): 5132-5164. doi: 10.1111/mec.16659
[8] 秦传新, 左涛, 于刚, 等. 环境DNA在水生生态系统生物量评估中的研究进展[J]. 南方水产科学, 2020, 16(5): 123-128. doi: 10.12131/20190256 [9] 舒璐, 林佳艳, 徐源, 等. 基于环境DNA宏条形码的洱海鱼类多样性研究[J]. 水生生物学报, 2020, 44(5): 1080-1086. [10] DEINER K, BIK H M, MACHLER E, et al. Environmental DNA metabarcoding: transforming how we survey animal and plant communities[J]. Mol Ecol, 2017, 26(21): 5872-5895. doi: 10.1111/mec.14350
[11] ALICE V, PIERRE T, CLAUDE M, et al. Next-generation monitoring of aquatic biodiversity using environmental DNA metabarcoding[J]. Mol Ecol, 2015, 25(4): 929-942.
[12] QUENTIN M, LYNSEY R H, MICHAEL S, et al. The multiple states of environmental DNA and what is known about their persistence in aquatic environments[J]. Environ Sci Technol, 2022, 56(9): 5322-5333. doi: 10.1021/acs.est.1c07638
[13] PAWLOWSKI J, KELLY-QUINN M, ALTERMATT F, et al. The future of biotic indices in the ecogenomic era: integrating (e)DNA metabarcoding in biological assessment of aquatic ecosystems[J]. Sci Total Environ, 2018, 637/638(1): 1295-1310.
[14] TABERLET P, COISSAC E, HAJIBABAEI M, et al. Environmental DNA[J]. Mol Ecol, 2012, 21(8): 1789-1793. doi: 10.1111/j.1365-294X.2012.05542.x
[15] SHU L, LUDWIG A, PENG Z G. Standards for methods utilizing environmental DNA for detection of fish species[J]. Genes-Basel, 2020, 11(3): 296. doi: 10.3390/genes11030296
[16] BOHMANN K, EVANS A, GILBERT M T P, et al. Environmental DNA for wildlife biology and biodiversity monitoring[J]. Trends Ecol Evol, 2014, 29(6): 358-367. doi: 10.1016/j.tree.2014.04.003
[17] TAKAHARA T, MINAMOTO T, YAMANAKA H, et al. Estimation of fish biomass using environmental DNA[J]. PLoS One, 2012, 7(4): e35868. doi: 10.1371/journal.pone.0035868
[18] THOMSEN P F, KIELGAST J, IVERSEN L L, et al. Detection of a diverse marine fish fauna using environmental DNA from seawater samples[J]. PLoS One, 2012, 7(8): e41732. doi: 10.1371/journal.pone.0041732
[19] BELLE C C, STOECKLE B C, GEIST J. Taxonomic and geographical representation of freshwater environmental DNA research in aquatic conservation[J]. Aquat Conserv, 2019, 29(11): 1996-2009. doi: 10.1002/aqc.3208
[20] 赵明, 赵梦迪, 马春艳, 等. 环境DNA在水域生态中的研究进展[J]. 中国水产科学, 2018, 25(4): 714-720. [21] TSUJI S, TAKAHARA T, DOI H, et al. The detection of aquatic macroorganisms using environmental DNA analysis: a review of methods for collection, extraction, and detection[J]. Environ DNA, 2019, 1(2): 99-108. doi: 10.1002/edn3.21
[22] 《中国河湖大典》编纂委员会. 中国河湖大典 珠江卷[M]. 北京: 中国水利水电出版社, 2013: 1-10. [23] 张迎秋, 黄稻田, 李新辉, 等. 西江鱼类群落结构和环境影响分析[J]. 南方水产科学, 2020, 16(1): 42-52. [24] XING Y C, ZHANG C G, FAN E Y, et al. Freshwater fishes of China: species richness, endemism, threatened species and conservation[J]. Divers Distrib, 2016, 22(3): 358-370. doi: 10.1111/ddi.12399
[25] 李捷, 李新辉, 贾晓平, 等. 西江鱼类群落多样性及其演变[J]. 中国水产科学, 2010, 17(2): 298-311. [26] 李跃飞, 李新辉, 杨计平, 等. 珠江干流长洲水利枢纽蓄水后珠江鳡鱼 (Elopichthys bambusa) 早期资源现状[J]. 湖泊科学, 2015, 27(5): 917-924. [27] 帅方敏, 李新辉, 刘乾甫, 等. 珠江水系鱼类群落多样性空间分布格局[J]. 生态学报, 2017, 37(9): 3182-3192. [28] 盛强, 茹辉军, 李云峰, 等. 中国国家级水产种质资源保护区分布格局现状与分析[J]. 水产学报, 2019, 43(1): 62-80. [29] 杨君兴, 潘晓赋, 陈小勇, 等. 中国淡水鱼类人工增殖放流现状[J]. 动物学研究, 2013, 34(4): 267-280. [30] OWEN S W, CREU P, MAGDALENA G, et al. DNA metabarcoding of littoral hard-bottom communities: high diversity and database gaps revealed by two molecular markers[J]. PeerJ, 2018, 6: e4705. doi: 10.7717/peerj.4705
[31] CHEN W T, LI C, YANG J P, et al. Temporal species-level composition of larvae resources in the lower Pearl River drainage and implications for species' reproductive cycles[J]. Gene, 2021, 776: 145351. doi: 10.1016/j.gene.2020.145351
[32] 王梦, 杨鑫, 王维, 等. 基于eDNA技术的长江上游珍稀特有鱼类国家级自然保护区重庆段鱼类多样性研究[J]. 水生生物学报, 2022, 46(1): 2-16. [33] 郑慈英. 珠江鱼类志[M]. 北京: 科学出版社, 1989: 77-367. [34] 张春光, 赵亚辉. 中国内陆鱼类物种与分布[M]. 北京: 科学出版社, 2016: 210-213. [35] DIXON P. VEGAN, a package of R functions for community ecology[J]. J Veg Sci, 2003, 14(6): 927-930. doi: 10.1111/j.1654-1103.2003.tb02228.x
[36] 李捷, 李新辉, 谭细畅, 等. 广东肇庆西江珍稀鱼类省级自然保护区鱼类多样性[J]. 湖泊科学, 2009, 21(4): 556-562. doi: 10.3321/j.issn:1003-5427.2009.04.015 [37] 李跃飞, 李新辉, 谭细畅, 等. 西江肇庆江段渔业资源现状及其变化[J]. 水利渔业, 2008, 28(2): 80-83. [38] HEBERT P D, CYWINSKA A, BALL S L, et al. Biological identifications through DNA barcodes[J]. Proc R Soc B, 2003, 270(1512): 313-321. doi: 10.1098/rspb.2002.2218
[39] 蒋佩文, 李敏, 张帅, 等. 基于线粒体COI和12S rDNA基因构建珠江河口鱼类DNA宏条形码数据库[J]. 南方水产科学, 2022, 18(3): 13-21. [40] 郜星晨, 姜伟. 三峡库区常见鱼类DNA条形码本地BLAST数据库的构建和应用[J]. 基因组学与应用生物学, 2021, 40(5/6): 1952-1960. [41] 乐佩琦. 中国动物志. 硬骨鱼纲 鲤形目 中卷[M]. 北京: 科学出版社, 2000: 1-16. [42] 刘亚秋, 李新辉, 李跃飞, 等. 西江广东鲂 (Megalobrama terminalis) 繁殖生物学及繁殖策略[J]. 湖泊科学, 2021, 33(1): 232-241. [43] GOUTTE A, MOLBERT N, GUÉRIN S, et al. Monitoring freshwater fish communities in large rivers using environmental DNA metabarcoding and a long-term electrofishing survey[J]. J Fish Biol, 2020, 97(2): 444-452. doi: 10.1111/jfb.14383
[44] LAMY T, PITZ K J, CHAVEZ F P, et al. Environmental DNA reveals the fine-grained and hierarchical spatial structure of kelp forest fish communities[J]. Sci Rep-UK, 2021, 11(1): 14439. doi: 10.1038/s41598-021-93859-5
[45] CIVADE R, DEJEAN T, VALENTINI A, et al. Spatial representativeness of environmental DNA metabarcoding signal for fish biodiversity assessment in a natural freshwater system[J]. PLoS One, 2016, 11(6): e0157366.
[46] RUPERT A C, JUDITH B, OWEN S W, et al. Non-specific amplification compromises environmental DNA metabarcoding with COI[J]. Methods Ecol Evol, 2019, 10(11): 1985-2001. doi: 10.1111/2041-210X.13276
[47] 刘军, 赵良杰, 凡迎春, 等. 鱼类环境DNA研究中通用引物的筛选验证[J]. 淡水渔业, 2016, 46(1): 9-17. [48] MACKENZIE D I, NICHOLS J D, LACHMAN G B, et al. Estimating site occupancy rates when detection probabilities are less than one[J]. Ecology, 2002, 83(8): 2248-2255. doi: 10.1890/0012-9658(2002)083[2248:ESORWD]2.0.CO;2
[49] GU W D, SWIHART R K. Absent or undetected? Effects of non-detection of species occurrence on wildlife–habitat models[J]. Biol Conserv, 2004, 116(2): 195-203. doi: 10.1016/S0006-3207(03)00190-3
[50] GOTELLI N J, COLWELL R K. Estimating species richness[M]//MAGURRAN A E, McGILL B J. Frontiers in measuring biodiversity. New York: Oxford University Press, 2011: 39-54.
[51] CRISTESCU M E, HEBERT P D N. Uses and misuses of environmental DNA in biodiversity science and conservation[J]. Annu Rev Ecol Evol S, 2018, 49(1): 209-230. doi: 10.1146/annurev-ecolsys-110617-062306
[52] ZOU K S, CHEN J W, RUAN H T, et al. eDNA metabarcoding as a promising conservation tool for monitoring fish diversity in a coastal wetland of the Pearl River Estuary compared to bottom trawling[J]. Sci Total Environ, 2020, 702: 134704. doi: 10.1016/j.scitotenv.2019.134704
[53] ZHANG S N, ZHAO J D, YAO M. A comprehensive and comparative evaluation of primers for metabarcoding eDNA from fish[J]. Methods Ecol Evol, 2020, 11(12): 1609-1625. doi: 10.1111/2041-210X.13485
[54] SHIN-ICHIRO O, HIDEYUKI D, KEI M, et al. Environmental DNA metabarcoding for biodiversity monitoring of a highly diverse tropical fish community in a coral reef lagoon: estimation of species richness and detection of habitat segregation[J]. Environ DNA, 2021, 3(1): 55-69. doi: 10.1002/edn3.132
[55] 熊美华, 杨志, 胡兴坤, 等. 长江中游监利江段鱼类群落结构研究[J]. 长江流域资源与环境, 2019, 28(9): 2109-2118. [56] 武智, 李跃飞, 朱书礼, 等. 基于渔业声学调查的珠江东塔产卵场鱼类栖息地适宜性研究[J]. 南方水产科学, 2023, 19(3): 11-18. [57] 蒋佩文, 李敏, 张帅, 等. 基于环境DNA宏条码和底拖网的珠江河口鱼类多样性[J]. 水生生物学报, 2022, 46(11): 1701-1711. [58] 谭细畅, 李新辉, 李跃飞, 等. 尼罗罗非鱼早期发育形态及其在珠江水系的空间分布[J]. 生物安全学报, 2012, 21(4): 295-299. [59] 顾党恩, 牟希东, 罗渡, 等. 广东省主要水系罗非鱼的建群状况[J]. 生物安全学报, 2012, 21(4): 277-282. [60] TONY D, ALICE V, ANTOINE D, et al. Persistence of environmental DNA in freshwater ecosystems[J]. PLoS One, 2012, 6(8): e23398.
[61] FICETOLA G F, MIAUD C, POMPANON F, et al. Species detection using environmental DNA from water samples[J]. Biol Lett, 2008, 4(4): 423-425. doi: 10.1098/rsbl.2008.0118
[62] HOWALD G, DONLAN C J, GALVAN J P, et al. Invasive rodent eradication on islands[J]. Conserv Biol, 2007, 21(5): 1258-1268. doi: 10.1111/j.1523-1739.2007.00755.x
[63] BOOTHROYD M, MANDRAK N E, FOX M, et al. Environmental DNA (eDNA) detection and habitat occupancy of threatened spotted gar (Lepisosteus oculatus)[J]. Aquat Conserv, 2016, 26(6): 1107-1119. doi: 10.1002/aqc.2617
[64] JANOSIK A M, JOHNSTON C E. Environmental DNA as an effective tool for detection of imperiled fishes[J]. Environ Biol Fish, 2015, 98(8): 1889-1893. doi: 10.1007/s10641-015-0405-5
[65] 甘西, 蓝家湖, 吴铁军, 等. 中国南方淡水鱼类原色图鉴[M]. 郑州: 河南科学技术出版社, 2017: 75. [66] VALDIVIA-CARRILLO T, ROCHA-OLIVARES A, REYES-BONILLA H, et al. Integrating eDNA metabarcoding and simultaneous underwater visual surveys to describe complex fish communities in a marine biodiversity hotspot[J]. Mol Ecol Resour, 2021, 21(5): 1558-1574. doi: 10.1111/1755-0998.13375
[67] CILLEROS K, VALENTINI A, ALLARD L, et al. Unlocking biodiversity and conservation studies in high-diversity environments using environmental DNA (eDNA): a test with Guianese freshwater fishes[J]. Mol Ecol Resour, 2019, 19(1): 27-46. doi: 10.1111/1755-0998.12900
-
期刊类型引用(2)
1. 杨艳,蓝一,刘佳敏,王茜. 渔业生物环境DNA宏条形码数据库研究进展. 湖北农业科学. 2025(01): 174-180 .  百度学术
百度学术
2. 李筱芹,吴开阳,倪达富,杨丽亚,鲁桃秀,张连博,邓华堂,吴彤飞,何荣超,付梅,姚维志,吕红健. 基于环境DNA技术的梯级水坝对长江上游重要支流鱼类多样性的影响研究——以綦江为例. 生态学报. 2024(19): 8865-8883 .  百度学术
百度学术
其他类型引用(2)
-
其他相关附件
-
PDF格式
20230111附录A 点击下载(649KB)
-



 下载:
下载:

 粤公网安备 44010502001741号
粤公网安备 44010502001741号
